Moleculaire weergave van een grofkorrelig model op basis van de oorspronkelijke structuur van M13 major coat-eiwitten Credit: SUTD
Atomistische simulaties zijn een krachtig hulpmiddel om de beweging en interacties van atomen en moleculen te bestuderen. Bij veel biologische processen zijn effecten op grote schaal, bijvoorbeeld assemblage van grote virussen tot nanodeeltjes, belangrijk. De assemblageprocessen van deze grote virussen zijn van fundamenteel belang voor het ontwerp van veel apparaten en op virale proteïne gerichte therapieën. De tijd- en lengteschaal van deze assemblageprocessen zijn echter meestal te groot voor simulaties met moleculaire resolutie.
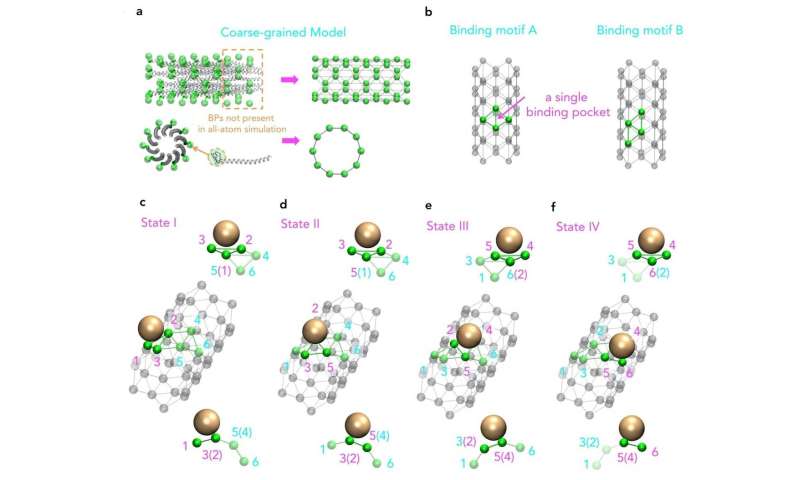
Bovendien zijn virusstructuren, zoals M13, nog steeds onbereikbaar, ook al maakt een toename van de rekenkracht complexere en langere simulaties mogelijk. Daarom heeft een onderzoeksgroep van de Singapore University of Technology and Design (SUTD) en het Massachusetts Institute of Technology (MIT) een procedure ontwikkeld die grootschalige assemblageprocessen koppelt aan moleculaire simulaties. Assistent Prof Desmond Loke van SUTD’s Science, Mathematics and Technology-cluster zei: “Voor de simulatie van M13 zijn we begonnen met verschillende sets krachtvelden. Er werden geschikte krachtvelden gekozen en deze werden gebruikt als input voor een molecuul-dynamica-simulatie met de grove -grain model ontworpen om het belangrijkste patroon van het assemblageproces vast te leggen. “
“Hoewel we weten dat M13-gebaseerde fabricage fundamenteel kan worden aangestuurd door nanodeeltjes-peptide-interacties, wat ook een sleutelprincipe kan zijn achter M13-type bio-engineering, hebben we weinig kennis over hoe herhaalde patronen van korte-eind-peptiden op een M13-oppervlak zijn eigenlijk bij deze interacties betrokken. Om dit te bestuderen, moeten we idealiter een volledige structuur van het virale manteleiwit opnemen, wat een moeilijke taak is voor de huidige state-of-the-art moleculaire dynamica-simulaties, “voegt Dr. Lunna Li toe. , eerste auteur van het artikel.
De procedure stelt gebruikers in staat om verschillende soorten nanodeeltjes toe te voegen aan een oplossing, op een realistisch niveau. Geïnspireerd door deze procedure konden universitair docent Loke en zijn collega’s een grootschalig virus simuleren met nanodeeltjes en in een oplossing voor vijftig nanoseconden.
Dr. Li zei: “De virusstructuur en -oplossing bevatten in totaal ongeveer 700.000 atomen.” Gezien de vorm en grootte van de kenmerken, kan de complexiteit van deze simulatie groter zijn dan elke eerdere simulatie.
“Een simulatie uitgevoerd in microseconden zou mogelijk zijn geweest als een kleiner M13-model was gebruikt, maar het kan de moeite waard zijn om de tijd te verkorten om daadwerkelijk te observeren hoe de volledige structuur de assemblage tussen de M13 en nanodeeltjes kan beïnvloeden”, legt assistent Prof Loke uit.
Lunna Li et al, Simulatie van selectieve binding van een biologische sjabloon aan een architectuur op nanoschaal: een kernconcept van een klemgebaseerde binding-pocket-favoriete N-terminale domeinsamenstelling, Nanoschaal (2020). DOI: 10.1039 / D0NR07320B
Nanoschaal
Geleverd door Singapore University of Technology and Design